欧洲千里光SvAPETALA1基因的克隆及功能分析
郝燕敏,陈柯俐,冯丽君,李菲菲,崔敏龙,朴春兰
(浙江农林大学 园艺科学学院,浙江 杭州 311300)
花发育是植物生长发育阶段的重要组成部分,过程虽然复杂,但十分有序。花发育的整个过程不仅受到光照、温度和湿度等外源因素的影响, 而且内源基因的相互作用也是决定开花调节机制的关键性因子[1-2]。MADS-box基因是一种植物特有的转录调控因子,在所有器官的形态发生乃至植物整个生命周期中发挥作用,例如:叶形态发生,花和果实发育以及种子发育[3]。其中,APETALA1 (AP1)类基因除了作为花分生组织特征基因[4],还表现为花器官特征基因,通过调控花器官的分化影响花发育[5-6]。反映这一特性的是ABC模型,A类基因控制萼片和花瓣的形成,B类基因控制花瓣和雄蕊的形成,C类基因控制雄蕊和心皮的形成[7]。AP1基因作为A类基因,调控萼片和花瓣的分化,并且与C类基因相互拮抗[8-9]。由于AP1类基因在花发育调控网络中的重要作用,使得不同物种中AP1类基因的研究更具有意义与价值。目前,在拟南芥Arabidopsis thaliana[8]、金鱼草Antirrhinum majus[5]和番茄Solanum lycopersicum[10]等植物中,对AP1类基因功能进行了较深入的研究,但是在菊科Asteraceae植物中的研究还有限。菊科植物具有典型的头状花序[11],花序外侧舌状花两侧对称,缺乏功能性雄蕊,而中央的管状花则是辐射对称的两性花,形态结构复杂。特殊的花序结构不仅提升了虫媒传粉的效率,也增强了菊科植物的观赏价值[12]。近年来,对于菊科植物,例如菊花Chrysanthemum morifolium[13]、非洲菊Gerbera hybrida[14]和向日葵Helianthus annuus[15]等的研究表明:复杂的头状花序对于研究花器官发育的遗传调控具有重要意义。因此,本研究克隆了菊科欧洲千里光Senecio vulgaris的SvAP1基因。由于菊科植物遗传转化体系较为复杂、转化周期长且转化效率低,故将SvAP1基因异源转化茄科Solanaceae龙葵Solanum nigrum中进行功能预测与分析,旨在为菊科植物AP1类基因的分子机制提供理论基础。
1 材料与方法
1.1 材料
将欧洲千里光和龙葵种子均在 25 ℃、光周期 16 h (白天)/8 h (黑夜)条件下播种于人工气候室。取欧洲千里光和龙葵的不同组织样品,包括新鲜的根、茎、叶和花完全展开时期的花序等,所有样品标记分装后置于液氮中速冻,保存于-80 ℃备用。
1.2 基因克隆
取欧洲千里光花完全展开时期约0.1 g的花序为材料,利用Eastep® Super总RNA提取试剂盒(普洛麦格生物产品有限公司,上海)提取总RNA,并用质量分数为1%的琼脂糖凝胶电泳和超微量紫外分光光度计(NanoDrop2000,赛默飞世尔科技公司,美国)对RNA样品的完整性和浓度进行检测。利用反转录试剂盒EasyScript®First-Strand cDNA Synthesis SuperMix (全式金生物技术有限公司,北京),参照说明书合成cDNA,产物储存于-20 ℃ 备用。
将欧洲千里光早期头状花序样品材料送至上海翰宇生物科技有限公司获得转录组数据。根据欧洲千里光转录组数据分析得到SvAP1基因序列。利用美国国家生物技术信息中心(NCBI,https://www.ncbi.nlm.nih.gov/) Primer-BLAST设计特异性引物,并在正向和反向引物中分别添加XbaⅠ和SacⅠ限制性内切酶酶切位点及保护碱基,特异性引物SvAP1-F和SvAP1-R由杭州有康生物科技有限公司合成(表1)。以欧洲千里光cDNA为模板,进行聚合酶链式反应(PCR)扩增。PCR扩增体系为:97 ℃预变性3 min;95 ℃变性 40 s,59 ℃ 退火 40 s,72 ℃ 延伸 1 min,35 次循环;72 ℃ 总延伸 10 min。PCR 扩增片段经切胶回收纯化后连接至pEASY-T1 Simple载体(全式金生物技术有限公司,北京),并转化大肠埃希菌Escherichia coliDH5α感受态细胞中(唯地生物技术有限公司,上海),根据蓝白斑筛选以及菌落PCR验证,测序获得目的基因。
1.3 序列比对及系统进化树构建
将目的基因在NCBI网站上进行blastx检索,下载各物种中与SvAP1同源性较高基因氨基酸FASTA格式文件;利用ClustalX(2.1)[16]及MEGA-X(10.1.8)[17]软件,采用邻接法(neighbor-joining, NJ),校验参数Bootstrap为1 000次,进行多序列比对以及系统进化树的构建,并用GeneDoc(2.7.0)软件对多序列比对进行修饰美化。
1.4 组织特异性表达分析
分别提取欧洲千里光的不同组织(根、茎、叶和花序)的RNA并反转为cDNA。以cDNA为模板,进行实时荧光定量PCR (qRT-PCR)。根据引物设计原则设计特异引物qSvAP1-F、qSvAP1-R,内参基因引物为Sv18s-F、Sv18s-R(表1),参照 qPCR 试剂盒TransStart®Tip Green qPCR SuperMix(全式金生物技术有限公司,北京)说明书,反应体系为:cDNA(稀释 10 倍)1 μL,2×TransStart®Tip Geen qPCR SurperMix 5 μL,上下游引物 (10 μm·L-1)各 0.2 μL,双蒸水 3.6 μL,95 ℃ 预变性 30 s,95℃ 变性 5 s,60 ℃ 复性30 s,共进行40个循环。试验设置3个重复反应,并采用2-ΔΔCt法计算各部位SvAP1的相对表达量,通过 SPSS 19.0[18]软件进行单因素方差分析(ANOVA),默认置信区间为95%。

表1 基因克隆与分子鉴定所用引物序列Table 1 Primer sequences for gene cloning and molecular identification
1.5 超表达载体的构建及农杆菌 Agrobacterium tumefaciens介导转化龙葵
应用XbaⅠ和SacⅠ限制性内切酶酶切pBI121超表达载体与pEASY-T1Simple-SvAP1重组质粒,将酶切后的目的片段与载体片段进行酶连,将酶连产物转化至大肠埃希菌感受态DH5α中,挑选单克隆进行菌落PCR鉴定,提取质粒并进行单双酶切检验后转化到农杆菌GV3101中,PCR鉴定获得阳性菌落,然后采用农杆菌介导的叶盘法进行龙葵的遗传转化。
1.6 转基因龙葵筛选及分子鉴定
利用特异性引物SvAP1-F、SvAP1-R (表1)进行PCR以及RT-PCR反应,对转基因龙葵进行进一步的鉴定及表达分析。采用十二烷基苯磺酸钠(SDS)法提取野生型及转基因龙葵基因组DNA,使用卡那霉素引物NPTⅡ-F、NPTⅡ-R 及特异性引物SvAP1-F、SvAP1-R (表1)进行 PCR 检测;提取野生型及转基因龙葵幼嫩叶片的RNA,反转录后得到cDNA。以此为模板,使用内参引物Sn18s-F、Sn18s-R以及特异性引物SvAP1-F、SvAP1-R (表1),进行半定量RT-PCR反应。反应体系为:97 ℃预变性3 min;95 ℃变性 40 s,59 ℃ 退火 40 s,72 ℃ 延伸 1 min,30 次循环;72 ℃ 总延伸 10 min。
1.7 转基因龙葵雌蕊组织学染色观察
解剖盛花期野生型及转基因龙葵花器官,以雌蕊为材料,进行纵向石蜡切片,探究其内部结构的变化。石蜡切片制作参照祁宏英等[19]的方法。主要步骤包括:①材料固定。利用真空泵将材料中的气体去除后将其放入FAA固定液(无水乙醇、冰醋酸、甲醛和双蒸水体积比为10∶1∶2∶7)固定24.0 h以上。②脱水、透明。固定材料取出后用体积分数为50%乙醇溶液冲洗,然后在一系列由低到高体积分数的乙醇溶液中逐级脱水,每级1.5 h,纯浓度1.0 h。将脱尽水的材料按照不同比例的无水乙醇和二甲苯逐级过渡到纯二甲苯溶液,使得材料中的无水乙醇被二甲苯替代达到透明的效果,每级1.0 h。③浸蜡。二甲苯后加入少量碎蜡,放入45 ℃ 恒温箱过夜,次日早上继续加入碎蜡,6.0 h后移至60 ℃ 恒温箱,换入熔融的纯蜡,之后每日早晚各换入1次纯蜡,让石蜡慢慢渗透到材料中。换2~3 d效果较好。④包埋、切片、粘片。将融化的石蜡迅速加入包埋框中,放入材料。调整轮转式切片机(RM2235,徕卡显微系统有限公司,上海),切片厚度为8 μm,将切好的蜡带依次放入载玻片上,置于42 ℃ 恒温箱中烘片。⑤海氏铁矾-苏木精染色法染色及观察。经过脱蜡后采用海氏铁矾-苏木精染色法进行染色,并脱水、透明、树胶封片,用显微镜(EX20,舜宇仪器有限公司,宁波)观察。
2 结果与分析
2.1 基因克隆及序列同源性分析
以欧洲千里光的cDNA为模板,经PCR扩增并对扩增片段进行测序,测序结果显示:SvAP1基因开放阅读框(ORF)区由705 bp组成,编码234个氨基酸,与转录组数据相一致。从NCBI-blastx筛选出拟南芥、金鱼草、马铃薯Solanum tuberosum和甘菊Chrysanthemum lavandulifolium等植物中SvAP1的同源基因序列,进行同源性分析。结果表明:欧洲千里光SvAP1与甘菊ClAP1 (ADK94172.1)和菊花CDM8(AAO22981.1)同源性最高,分别为76.05%和75.21%。进一步分析发现:SvAP1具有典型的MIKC型MADS-box 基因结构,结构域由 MADS-box (M)、Intervening (I)、K-box (K)和 C-terminal (C)等 4 个部分组成。在C末端具有真双子叶植物AP1类基因2个较短且相对保守的基序(motif),其中之一为paleoAPETALA1 (paleoAP1)蛋白基序,另一个为FUL蛋白基序(图1A),与ClAP1和CDM8保持一致。利用MEGA-X软件构建欧洲千里光SvAP1氨基酸序列的系统进化树(图1B),结果显示:SvAP1与甘菊ClAP1、菊花CDM8、番茄SlFRUITFULLFUL(SlFUL) (NP_001294867.1)、马铃薯StAGL8 (XP_006345101.1)、辣 椒CapsicumannuumCaAGL8 (NP_001311552.1)、绒 毛 烟 草NicotianatomentosiformisNtAGL8(XP_009625854.1)、拟南芥AP1 (CAA78909.1)和金鱼草SQUAMOSA(SQUA) (CAA45228.1)处于同一个分支中,亲缘关系接近。
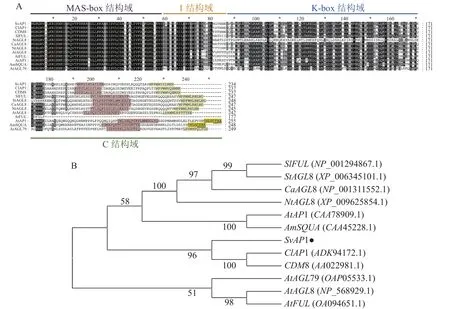
图1 欧洲千里光SvAP1氨基酸多序列比对以及系统进化树分析Figure 1 Amino acid sequence alignment and phylogenetic tree analysis of SvAP1 in S. vulgaris
2.2 组织特异性表达分析
通过qRT-PCR对欧洲千里光不同组织部位的表达水平进行分析。结果表明(图2):SvAP1在欧洲千里光茎、叶和花序中都有表达,其中SvAP1在花序中的表达水平高于在茎和叶。因此,初步推测SvAP1在营养生长和生殖生长中可能都起到一定的调控作用。

图2 SvAP1 在欧洲千里光不同部位的相对表达Figure 2 Relative expression of SvAP1 in different tissues of S.vulgaris
2.3 转基因龙葵筛选、鉴定及形态学观察
为了研究SvAP1的功能,通过农杆菌介导的遗传转化获得的9个独立抗性植株中,选取表型变化明显的3株抗性植株,提取DNA后进行目的基因和卡那霉素抗性基因的双重扩增。结果显示:扩增的大小均与预期相符合(图3A和图3B),表明筛选出的3株抗性植株为转基因抗性植株。以野生型植株SvAP1表达为对照,对转基因植株中SvAP1表达进行RT-PCR分析,结果显示(图4A):相比于对照植株,3株转基因抗性植株中的SvAP1表达量都出现了不同程度的升高。其中,SvAP1-3转基因龙葵中SvAP1表达量最低,SvAP1-4转基因龙葵SvAP1表达量较高,SvAP1-9转基因龙葵SvAP1表达量最高。由此可知:SvAP1在转基因抗性植株中得到了有效表达,可进行下一步的表型分析。观察筛选到的3株表型明显的转基因抗性植株发现:与同一时期野生型龙葵相比,转基因龙葵的茎和叶无明显变化,而花器官发育异常且果实数目减少(图4B)。

图3 野生型及转基因龙葵 PCR 检测Figure 3 PCR detection of wild type S. nigrum and different transgenic lines

图4 野生型和转基因龙葵 RT-PCR 及表型分析Figure 4 RT-PCR and phenotypes analysis of wild type S. nigrumand different transgenic lines
正常的野生型龙葵花序由外到内依次为5个萼片、5个花瓣、5个雄蕊以及1个雌蕊,雌蕊被雄蕊包裹于最内轮,仅柱头部分可见(图5A)。形态学观察发现,转基因龙葵雌蕊发育异常,其中弱表型SvAP1-3转基因龙葵花序与野生型无明显差异(图5B);中表型SvAP1-4转基因龙葵子房明显膨大,将雄蕊挤压至花瓣一侧,且雌蕊花柱基部与子房顶部连接处膨胀(图5C);强表型SvAP1-9转基因龙葵雄蕊被膨大的子房挤压至向花瓣方向倾斜生长,雌蕊状组织增多(图5D)。

图5 野生型及转基因龙葵花序Figure 5 Inflorescence in wild type S. nigrum and different transgenic lines
2.4 转基因龙葵雌蕊组织学染色观察
为了进一步探究SvAP1的异位表达对雌蕊发育的影响,对野生型及强表型SvAP1-9转基因龙葵花器官进行解剖,并对雌蕊进行显微镜观察发现:野生型龙葵雌蕊包括柱头、花柱和子房,花柱中部以下被白色绒毛,基部与卵状子房相连(图6A);强表型SvAP1-9转基因龙葵花柱数目增多,子房膨大且有心皮组织增生冲破子房壁暴露于子房顶部,外侧有花柱包裹(图6B)。为了分析转基因龙葵雌蕊内部结构的变化,对野生型以及强表型转基因龙葵的雌蕊进行纵向石蜡切片观察,结果显示:野生型龙葵花柱基部与胎座相连,两者基本位于子房中轴线处,卵圆状胚珠经珠柄与胎座相连相对平均分布于胎座两侧(图6C);强表型SvAP1-9转基因龙葵子房膨大,子房顶部增生的心皮组织发育较为完全。进一步分析强表型SvAP1-9转基因龙葵增生的心皮组织细胞结构:中心部分与子房胎座组织细胞结构相类似,呈不规则卵圆状紧密分布;靠近外缘部分细胞明显变小且更加紧凑呈层状排列,与子房壁细胞结构相类似(图6D)。由此推测,强表型SvAP1-9转基因龙葵增生的心皮组织形成了类似子房的结构。综上所述推测:SvAP1在龙葵中的异位表达对雌蕊发育产生影响,可能造成子房膨大且花柱与子房数目增多。
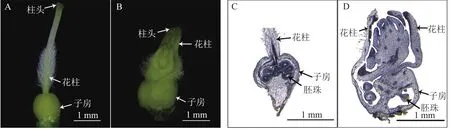
图6 野生型和转基因龙葵雌蕊及其石蜡切片Figure 6 Wild type S. nigrum and different transgenic lines pistil and their paraffin section
3 讨论
花是植物的生殖器官,被认为是植物进化中重要的形态创新,花器官的发育对于花形态的建成具有重要作用,而且受许多调控因子的影响[20]。菊科独特的头状花序结构使其成为研究植物花器官发育的重要材料。MADS-box家族基因在调控花分生组织和花器官发育中起着重要作用,因此其在菊科植物头状花序形成中的调节作用一直是近年来的研究热点[21]。其中,AP1类基因是花发育调节机制的调控枢纽,作为花器官特征基因在菊花[13]和碎米荠Cardamine hirsute[22]等植物中被研究报道。
真双子叶植物AP1类基因分为euAP1、euFRUITFULL(euFUL)和AGAMOUS-like79 (AGL79)等3个亚支,其中euAP1分支基因具有euAP1蛋白基序,euFUL与AGL79分支基因具有paleoAP1蛋白基序[23]。本研究所获得的欧洲千里光SvAP1基因在C末端段具有paleoAP1蛋白基序,且系统进化关系分析表明:SvAP1与ClAP1、CDM8、SlFUL、StAGL8、CaAGL8、NtAGL8、AP1和SQUA位于同一进化枝,其中与ClAP1和CDM8同源性最高。有报道指出:CDM8[13]、SlFUL[24]、CaAGL8[25]和NtAGL8[26]均属于euFUL类AP1分支,AP1[8]和SQUA[5]属于euAP1类AP1分支。综上所述可推测:SvAP1属于AP1类基因,即SQUA亚家族。LITT等[23]认为:多数具有paleoAP1蛋白基序的基因表达模式比具有euAP1蛋白基序的基因更为广泛,存在于营养组织和生殖组织,包括茎、叶、花分生组织、所有花器官和果实等。甘菊ClAP1研究较少,关于同源性较高的CDM8[13]研究表明:其在营养器官和生殖器官中都可以检测到表达,主要在茎、叶和花中表达,参与营养生长到生殖生长的调控。为了进一步研究SvAP1是否具有类似的表达模式,对欧洲千里光进行组织特异性表达分析。qRT-PCR反应显示:SvAP1基因表达模式比拟南芥AP1更为广泛,在欧洲千里光茎、叶和花中都可以检测到SvAP1表达,与CDM8相类似,可能对营养生长与生殖生长的发育都起到了调控作用。
BERBEL等[27]认为:AP1基因的“CFAA”基序并非是判断AP1类基因功能的决定性依据,不同的C端基序蛋白也可以发挥AP1基因相类似功能,“CFAA”只是增强了AP1类基因的活性,在多个物种中都有被报道,例如豌豆Pisum sativum的PEAM4[27]、大豆Glycine max的GmAP1[28]、百合Lilium longiflorum的LMADS6、LMADS7[29]和绒毛烟草的NtAGL8[26]等。因此,具有paleoAP1蛋白基序的基因也可能作为花器官特征基因影响花器官的发育。例如:LI等[30]发现:从红花玉兰Magnolia wufengensis中分离出的MawuAP1影响心皮及果实发育,主要在心皮的膨大中起作用,从而影响果实的发育;孙迎坤等[31]发现:山茶花Camellia japonica的CjAPL1转化拟南芥的阳性植株花器官发育异常,花柱和雄蕊数增加;邓柠檬等[32]发现:金钗石斛Dendrobium nobile的DnAPL1在转基因拟南芥中的表达会导致花器官数目增加,且萼片和花瓣形状发生变化。本研究发现:转基因龙葵花雌蕊发育异常,在强表型中可以观察到子房膨大且雌蕊状组织增多。因此推测,SvAP1在花器官形成中具有重要作用,且与ABC模型中A类基因超表达对于花器官发育造成的影响有所不同。在ABC模型中,A类基因的超表达会抑制C类基因的表达,从而对雄蕊与雌蕊的发育产生影响:雄蕊向花瓣同源异形转化且雌蕊转变为萼片状或叶片状器官。在本研究中,SvAP1在龙葵中的超表达同样影响了雌蕊的发育,但呈现出相对不同的表型,且雄蕊的发育无明显变化,这可能与欧洲千里光花器官调控机制与花序结构的复杂性有关。雌蕊的异常发育导致果实发育受到影响,在转基因龙葵中果实数目与同一时期野生型龙葵相比明显变少。
开花植物花调控网络十分庞大,不同基因之间存在较为复杂的相互作用关系。研究表明:在拟南芥中AP1 与SEPALLATA3 (SEP3)[32]、AGAMOUS(AG)[21]、FRUITFULL(FUL)[33]和UNUSUALFLORAL ORGANS(UFO)[34]等多种花器官发育相关基因存在相互作用,其中部分基因与心皮发育的调控有关。有研究报道:AP1类基因的异位表达可能对内源基因的表达产生了抑制或者促进作用,例如:毛白杨Populus tomentosa的AtAP1M3[35]和山茶花的CjAPL1[31]等。因此推测,SvAP1雌蕊发育异常也可能与基因之间的相互作用有关。为了进一步验证SvAP1的异位表达是否对于其他内源基因的表达产生了影响,从而共同导致雌蕊的变化,还需要进行转基因龙葵相关内源基因的表达分析。
本研究通过异源转化龙葵,初步预测了菊科欧洲千里光AP1类基因SvAP1作为花器官特征基因对花器官发育的影响。欧洲千里光组织特异性表达分析显示:SvAP1可能参与了营养生长与生殖生长的调控,其在龙葵中的异位表达却对龙葵的营养生长并没有起到明显的作用,推测这可能与物种之间的差异性有关,因此,为了深入探究SvAP1基因在欧洲千里光中的作用机制,需要后续研究进一步验证。

